Snakemake tutorial
What is snakemake
Snakemake는 특정 Pipeline을 만들기 위한 Python package이다.
가령 Cellline들로 부터 얻은 isoform 발현값들의 비교를 하는 파이프 라인을 짠다고 해보자. 파이프 라인은 다음과 같을 것이다.
Raw fastq files(paired end) > Tophat2 > cufflinks > comparison
이러한 일련의 과정을 수행하는데 사람이 일일히 다 수행하는 것은 굉장히 번거로운 일이다. 각각의 작업이 언제 끝날지도 모르기 때문이다.
따라서 이러한 파이프라인을 자동화 하여 수행시켜줄 수 있다면, 매우 편리할 것이다.
Snakemake는 지정한 Rule에 따라서 파이프라인의 과정을 자동화 해 준다.
snakemake는 python3 기반의 프로그램이다. 설치는 간단히 pypi를 이용하여.
pip3 install snakemake
커맨드를 이용하여 설치할 수 있다.
Mechanism of snakemake
스네이크 메이크는 Default하게 Snakefile이라는 파일을 입력으로 받는다.
Snakefile은 Rule들과 parameter들을 포함하고 있는 파일이다.
여기서 Rule이란 Pipeline에서 수행되는 각각의 과정들을 의미한다.
위에서 예시로 든 pipeline에서는
1. Tophat2로 fastq를 reference genome에 align하기
2. cufflinks로 FPKM값을 구하기
3. sample들간의 FPKM값의 차이를 구하기
등이 Rule이 될 수 있다.
Rule
Rule은 방금 언급했듯이 각각의 작업이다. Rule의 구조는 기본적으로
rule rule_name:
input: input_file
output: output_file
params: param1=param1, pram2=param2
shell: "command --option1 {params.param1} --option2 {params.param2} {input} {output}"
의 구조로 되어있다.
rule_name은 rule의 이름을 지정한다input은 input_file을 지칭한다. input_file이 존재하지 않을경우에는 일정시간(default:5seconds)를 기다린 후 없으면 pipeline의 수행을 abort시킨다.output은 output_file을 지칭한다. 해당 작업(rule)을 수행함으로써 만들어지는 output_file을 지칭한다.params는 해당 작업에 쓰일 parameter를 지칭한다. 뒤에서 언급하겠지만 Snakefile에서 설정하는 전역변수를 지정할 수 있다.shell은 수행할 작업 명령이다.shell대신run을 쓸수 있는데 이때는 command라인 명령어 대신 python3 코드를 수행할 수 있다
Construct DAG with rules
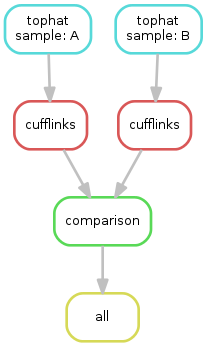
Snakemake는 이렇게 정의된 rule들로 DAG(Directed Acyclic Graph)를 만든다 가령 rule tophat와 cufflinks를 살펴보자.
rule tophat:
input: fwd="samples/raw/{sample}_1.fastq.gz", rev="samples/raw/{sample}_2.fastq.gz"
params: GFF=GFF, BowtieIndex=BowtieIndex, LibraryType=LibraryType
output: "samples/bam/{sample}.bam"
shell:"""
mkdir -p samples/tophat/{wildcards.sample}
tophat -p 10 -o samples/tophat/{wildcards.sample} -G {params.GFF} --library-type {params.LibraryType} {params.BowtieIndex} {input.fwd} {input.rev}
mv samples/tophat/{wildcards.sample}/accepted_hits.bam samples/bam/{wildcards.sample}.bam
"""
rule tophat의 경우 tophat으로 align을 시킨후 결과물인 samples/tophat/{sample}/accepted_hits.bam을 samples/bam/{sample}.bam으로 옮기는 것을 볼 수 있다.
rule cufflinks는 다음과 같다.
rule cufflinks:
input: "samples/bam/{sample}.bam"
params: GFF=GFF
output: "samples/cufflinks/{sample}/isoforms.fpkm_tracking"
shell: "cufflinks -p 10 -G {params.GFF} --output-dir samples/cufflinks/{wildcards.sample} {input}"
rule tophat의 output과 rule cufflinks의 input이 동일함을 볼 수 있다.
DAG를 만들기 위하여 각각의 rule들의 input과 output이 명시적으로 같아야 한다
snakemake는이런 input과 output의 관계를 통하여 DAG를 만들고 DAG에 따라서 작업을 자동적으로 수행하게 된다.
즉 rule cufflinks가 수행되기 위해서는 rule tophat의 output이 존재해야 된다는 것이다.
수행하는 예제의 DAG는 다음과 같다.
Parameters and working directory in snakemake
각종 parameter들은 python변수가 지정되듯이 지정될 수 있다.
BASE_DIR = "~/snakemake_exercise/"
WDIR = BASE_DIR + "tutorial"
LibraryType = "fr-firststrand"
snakemake가 수행되는 working directory는 workdir로 지정 될 수 있다.
workdir: WDIR
Wildcard in snakemake
아무런 작업도 수행하지 않은 상태에서 sample 폴더의 file tree를 살펴보자.
내가 cufflinks와 tophat에 계속 사용하고 싶은 이름은 A,B 이다.
`-- samples
`-- raw
|-- A_1.fastq.gz
|-- A_2.fastq.gz
|-- B_1.fastq.gz
`-- B_2.fastq.gz
glob_wildcards(wildcard)함수는 wildcard들을 파일로부터 추출해낸다
SAMPLES, = glob_wildcards(WDIR+"samples/raw/{sample}_1.fastq.gz")
이런식으로 내가 앞으로의 rule들에 사용할 wildcard들을 뽑아낼 수 있다.
이 함수의 반환값인 SAMPLES는 파이썬 리스트 객체이다. SAMPLES의 내용을 살펴보면
['A','B']
임을 확인할 수 있다.
cufflinks의 결과물인 FPKM들을 비교하는 rule인 rule comparison은 A와 B의 cufflinks의 수행결과가 모두 존재한 이후에 수행되어야 한다.
rule comparison:
input: expand("samples/cufflinks/{sample}/isoforms.fpkm_tracking", sample=SAMPLES)
output: "samples/comparison_result.csv"
run:
inputs = " ".join(input)
shell("python comprison.py "+inputs+" {output}")
이럴 경우에 expand(path_with_wildcards, wildcards)함수를 쓰면 된다. 이 함수는 지정해준 path에 와일드카드들을 매칭시켜준 결과물을 파이썬 리스트로 반환시켜준다.
위의 예시에서 input은
['samples/cufflinks/A/isoforms.fpkm_tracking', 'samples/cufflinks/B/isoforms.fpkm_tracking']
이 될것이다. 따라서 rule comparison은 A와 B의 output이 모두 나오고 나서야 수행될 것이다.
Mapping wildcards to inputs and outputs of rule.
rule comparison을 다시한번 살펴보자.
rule comparison:
input: expand("samples/cufflinks/{sample}/isoforms.fpkm_tracking", sample=SAMPLES)
expand()함수는 python list object의 값들인 wildcard들을 rule comparison에 맵핑해 줌과 동시에 여기에 연결되어있는 rule cufflinks의 output: samples/cufflinks/{sample}/isoforms.fpkm_tracking에도 매핑을 시켜준다.
이런 매핑은 연쇄적으로 rule cufflinks의 input과 rule tophat의 output,
그리고 input으로까지 와일드카드를 매핑할 것이고, 실제 samples/raw/{sample}_1.fastq.gz, samples/raw/{sample}_2.fastq.gz가 존재하는 것을 확인한후, 파이프라인을 실행할 것이다.
Rule all
파이프 라인의 최종 목적은 rule all의 input으로 지정할 수 있다. rule all은 output을 필요로 하지 않는다.
rule all:
input: "samples/comparison_result.csv"
Run snakemake
rule all으로 지정된 목적을 결과물로 만들어내기 위해서 snakemake를 수행하려면 Snakefile이 위치한 폴더에서
snakemake
커맨드를 입력하면 된다.
특정 rule만 실행하고 싶을 경우 output 파일 경로를 입력해 주면된다.
예를들어 rule tophat 만 실행하고 싶을 경우
snakemake samples/bam/{A,B}.bam
커맨드를 입력하면된다.
Make DAG image file
snakemake는 pipeline의 DAG를 dot file로 만들어준다 graphviz프로그램이 있으면 image파일로 만들 수 있다.
snakemake --dag | dot -Tpng > image_file_name.png
Use cluster
snakemake에서는 여러개의 잡이 병렬적으로 처리될 수 있도록 cluster 에서 잡을 수행할 수 있도록 할 수 있다.
cluster와 job management system이 있다는 가정하에(본 예제에서는 qsub을 사용한다)
snakemake --cluster "qsub --qsub-option arg" -j N
여기서 N은 한번에 최대 N개의 작업을 수행하도록 할 수 있게 만들겠다라는 의미이다.
Documentation
더 고급 기능등을 사용하고 싶다면, 공식 Documentation을 참고하도록 하자
https://bitbucket.org/snakemake/snakemake/wiki/Documentation