Методика вычисления индексов похожа. По этой причине мы рассмотрим только вариант получения данных по NDVI.
Для скачивания исходников космо снимка мы использовали 2 сайта:
https://scihub.copernicus.eu/dhus/#/home
https://apps.sentinel-hub.com/eo-browser/
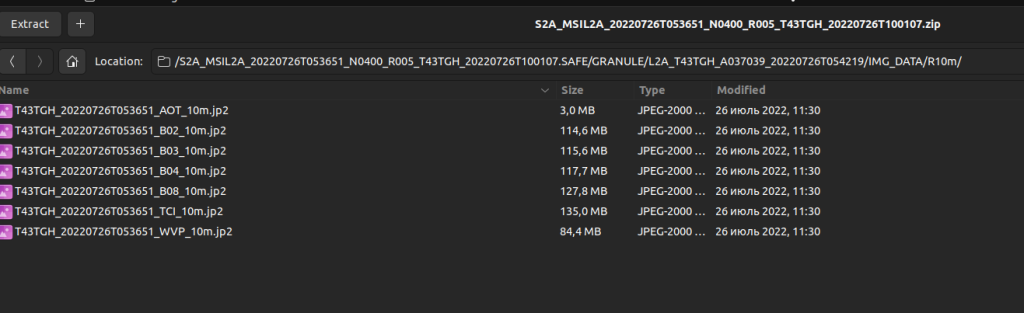
Для презентации я скачал участок в Исык-кульской области из первого сайта:
 Первый сайт выдаёт нам файлы в формате jp2, а второй в формате tiff.
Первый сайт выдаёт нам файлы в формате jp2, а второй в формате tiff.
- Для обработки использовался язык Python 3.10.6
- Так же должен быть установлен локально. Без локально установленного Gdal не установится в виртуальном окружении.
Библиотеки:
Gdal
Rasterio
Matplotlib
Numpy
Geopandas
После установки этих библиотек создал фай 1_from_jp2_to_tiff.py в котором прописали следующий код:
import rasterio
path = "./images/"
files = [
path + "B02.jp2", # Blue
path + "B03.jp2", # Green
path + "B04.jp2", # Red
path + "B08.jp2" # NIR
]
src = rasterio.open(files[0])
meta = src.meta
meta.update(count=len(files))
meta.update(driver="GTiff")
with rasterio.open("output/sentinel2.tif", "w", **meta) as dst:
for id, layer in enumerate(files, start=1):
with rasterio.open(layer) as src:
dst.write(src.read(1), id)
Результат этого скрипта: Переобразовывает файлы формата jp2 в один файл в формате tif.
Создал фай 2_calculatingNDVI.py в котором прописали следующий код:
import matplotlib.pyplot as plt
import numpy
import rasterio
image_file = "./output/sentinel2.tif"
with rasterio.open(image_file) as src:
band_red = src.read(3)
band_nir = src.read(4)
numpy.seterr(divide='ignore', invalid='ignore')
# Calculate NDVI
ndvi = (band_nir.astype(float) - band_red.astype(float)) / (band_nir + band_red)
min = numpy.nanmin(ndvi)
max = numpy.nanmax(ndvi)
mid = 0.1
fig = plt.figure(figsize=(20, 10))
ax = fig.add_subplot(111)
cmap = plt.cm.YlGn
cax = ax.imshow(ndvi, cmap=cmap, clim=(min, max), vmin=min, vmax=max)
ax.axis('on')
ax.set_title('Normalized Difference Vegetation Index', fontsize=18, fontweight='bold')
cbar = fig.colorbar(cax, orientation='horizontal', shrink=0.65)
ax.plot(20, 10)
plt.savefig('./output/result.png', bbox_inches='tight', transparent=True)
plt.show()
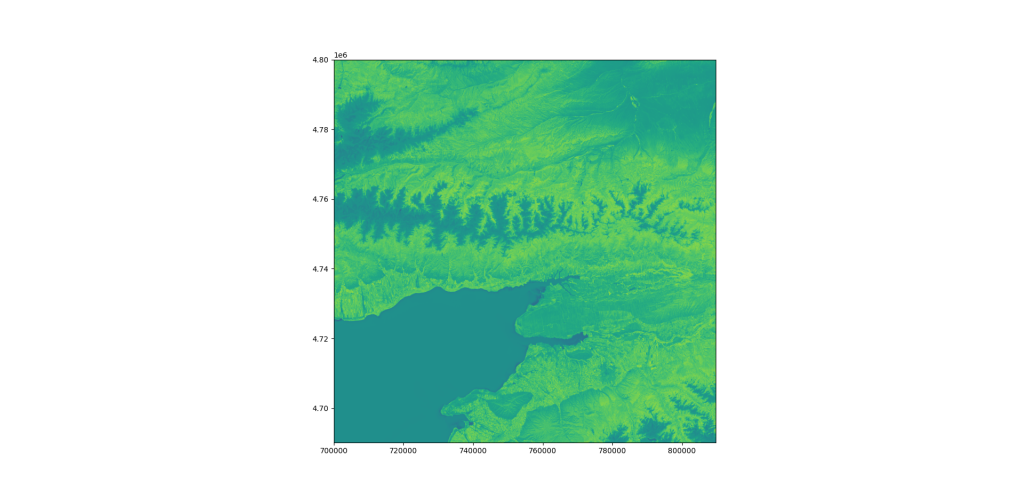
Результат этого скрипта: высчитывает NDVI получает картинку в формате png сохраняет.
Следующий код на вход берёт преобразованный из jp2 файлов tiif файл который у нас называется sentinel2.tif из него считывает 2 слоя red, nir. Высчитывает индекс NDVI и сохраняет его в формате tiff для дальнейшего использования:
import numpy
import rasterio
from rasterio import plot
import matplotlib.pyplot as plt
image_file = "./output/sentinel2.tif"
with rasterio.open(image_file) as src:
band_red = src.read(3)
band_nir = src.read(4)
# Allow division by zero
numpy.seterr(divide='ignore', invalid='ignore')
# Calculate NDVI
ndvi = (band_nir.astype(float) - band_red.astype(float)) / (band_nir + band_red)
# Set spatial characteristics of the output object to mirror the input
kwargs = src.meta
kwargs.update(
dtype=rasterio.float32,
count=1,
)
# Create the file
with rasterio.open('./output/2ndvi.tiff', 'w', **kwargs) as dst:
dst.write_band(1, ndvi.astype(rasterio.float32))
результат выглядит:
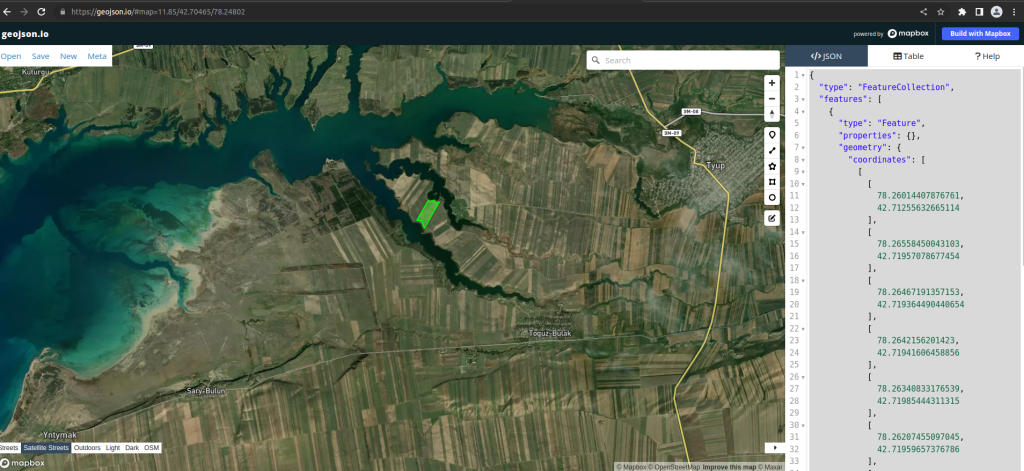
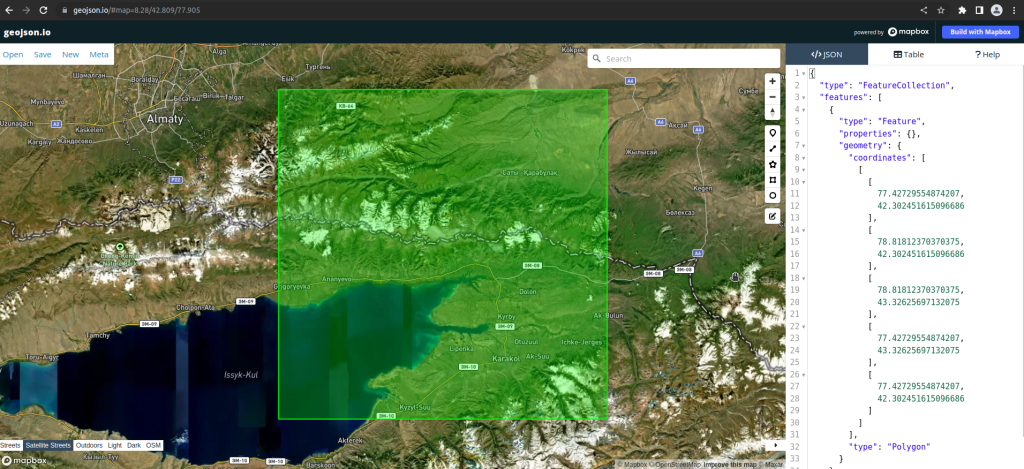
 Следующий шаг это вырезаем конкретный участок. Для этого на сайте geojson.io выделил участок и сохранил в файле cords.geojson:
Следующий шаг это вырезаем конкретный участок. Для этого на сайте geojson.io выделил участок и сохранил в файле cords.geojson:
{
"type": "FeatureCollection",
"features": [
{
"type": "Feature",
"properties": {},
"geometry": {
"coordinates": [
[
[
78.26014407876761,
42.71255632665114
],
[
78.26558450043103,
42.71957078677454
],
[
78.26467191357153,
42.719364490440654
],
[
78.2642156201423,
42.71941606458856
],
[
78.26340833176539,
42.71985444311315
],
[
78.26207455097045,
42.71959657376786
],
[
78.26147785956249,
42.71980286932967
],
[
78.25740631818894,
42.71459369640152
],
[
78.25828380555345,
42.714722641603316
],
[
78.25835400454343,
42.714490540046654
],
[
78.25937188988689,
42.71456790732867
],
[
78.25930169089679,
42.714155280710315
],
[
78.26014407876761,
42.71255632665114
]
]
],
"type": "Polygon"
}
}
]
}
После этого создал файл 4_cutting.py в котором прописал код:
from osgeo import gdal
def cutting_tiff(outputpath, inputpath, polygon):
gdal.Warp(destNameOrDestDS=f'{outputpath}',
srcDSOrSrcDSTab=inputpath,
cutlineDSName=f'{polygon}',
cropToCutline=True,
copyMetadata=True,
dstNodata=0)
cutting_tiff(outputpath='./output/cuttedNDVI.tiff', inputpath='./output/2ndvi.tiff', polygon='./cords.geojson')
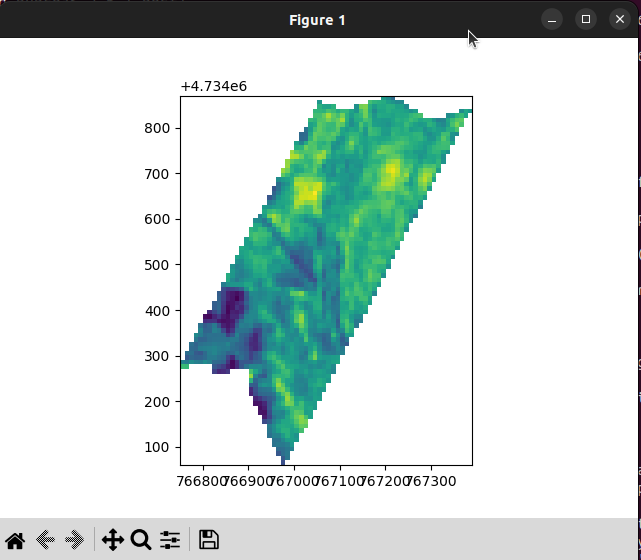
результат этого скрипта обрезал из tiff файла 2ndvi.tiff заданный участок:
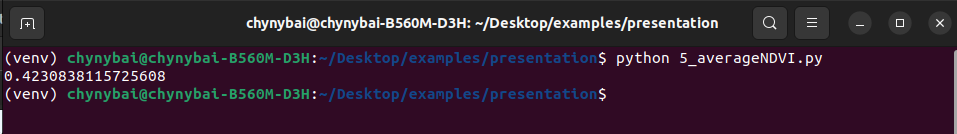
На данный момент у нас есть tiff файл с высчитанным NDVI и для вычисления среднего показателя использовал ниже указанный код:
import numpy as np
import rasterio
def get_region_of_interest(ndvi, multiplier=1/2):
# undo the background adjustment
region = ndvi.copy()
region = np.where(region == -255, 0, region)
# mean of center rows
center_row1 = np.mean(region[int((multiplier) *len(region))])
center_row2 = np.mean(region[int((multiplier) *len(region))+1])
# mean of both rows
mean = (center_row1.copy()+center_row2.copy())/2
return mean
my_file = rasterio.open('./output/2ndvi.tiff')
ndvi = my_file.read(1).astype('float64')
print(get_region_of_interest(ndvi=ndvi))
Результат данного скрипта:
Для этого понадобиться библиотека geopandas. Скрипт принимает файл который был обрезан по заданному участку (cuttedNDVI.tiff) и выдаёт как результат geojson файл в котором прописанны координаты и показатель индекса конкретного координата. Коде го выглядит следующим образом:
import time
from colorsys import hsv_to_rgb
import geopandas as gp
import rasterio
from rasterio.features import shapes
start = time.time()
tiff_name = './output/cuttedNDVI.tiff'
data = rasterio.open(tiff_name).meta
c = str(data['crs'])
c_s = c.split(':')
mask = None
with rasterio.open(tiff_name) as src:
image = src.read(1) # first band
results = (
{'properties': {'NDVI': v}, 'geometry': s}
for i, (s, v) in enumerate(shapes(image, mask=mask, transform=data['transform'])))
geoms = list(results)
gpd_polygonized_raster = gp.GeoDataFrame.from_features(geoms, crs=c)
gpd_polygonized_raster = gpd_polygonized_raster[gpd_polygonized_raster['NDVI']>0]
def pseudocolor(val, minval, maxval):
""" Convert val in range minval..maxval to the range 0..120 degrees which
correspond to the colors Red and Green in the HSV colorspace.
"""
h = (float(val-minval) / (maxval-minval)) * 120
# Convert hsv color (h,1,1) to its rgb equivalent.
# Note: hsv_to_rgb() function expects h to be in the range 0..1 not 0..360
r, g, b = hsv_to_rgb(h/360, 1., 1.)
return int(r*255), int(g*255), int(b*255)
minval = 0
maxval = 1
def rgb_to_hex(rgb):
return '%02x%02x%02x' % rgb
for i, row in gpd_polygonized_raster.iterrows():
gpd_polygonized_raster.loc[i, ('color')] = rgb_to_hex(pseudocolor(row['NDVI'], minval, maxval))
gpd_polygonized_raster['id'] = gpd_polygonized_raster.index
crs_sys = 'epsg:' + c_s[1]
gpd_polygonized_raster['geometry'] = gpd_polygonized_raster['geometry'].to_crs({'init': crs_sys})
gpd_polygonized_raster.to_file('result.geojson', driver='GeoJSON')
print(time.time() - start)
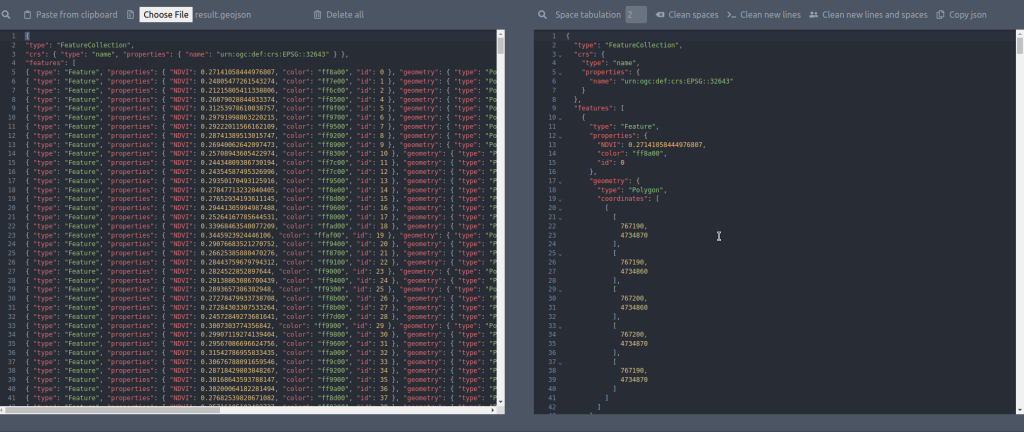
Результат:
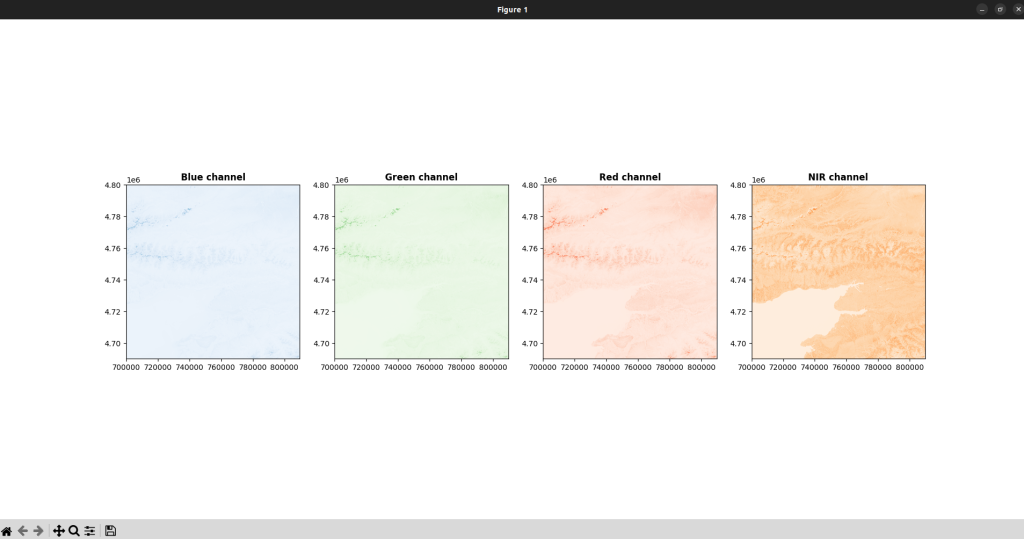
Код данного действия:
import rasterio
from rasterio.plot import show
import matplotlib.pyplot as plt
image_file = "./output/sentinel2.tif"
src = rasterio.open(image_file)
fig, (axb, axg, axr, axn) = plt.subplots(1,4, figsize=(24,8))
show((src, 1), ax=axb, cmap='Blues', title='Blue channel')
show((src, 2), ax=axg, cmap='Greens', title='Green channel')
show((src, 3), ax=axr, cmap='Reds', title='Red channel')
show((src, 4), ax=axn, cmap='Oranges', title='NIR channel')
plt.show()
при запуске этого кода результат будет следующим:
Создал файл 9_from_tiff_to_png.py в котором прописал код:
import matplotlib.pyplot as plt
import numpy
import rasterio
image_file = "./output/cuttedNDVI.tiff"
with rasterio.open(image_file) as f:
image = f.read(1)
fig = plt.figure(figsize=(20, 10))
ax = fig.add_subplot(111)
cmap = plt.cm.YlGn
cax = ax.imshow(image, cmap=cmap)
ax.axis('on')
ax.set_title('Normalized Difference Vegetation Index', fontsize=18, fontweight='bold')
cbar = fig.colorbar(cax, orientation='horizontal', shrink=0.65)
ax.plot(20, 10)
plt.savefig('./output/cuttedresult.png', bbox_inches='tight', transparent=True)
plt.show()
После запуска кода выведется результат и сохранит этот файл в папку output: